
导师队伍
孙德恩
邮箱:deen.sun@pku.edu.cn
地址:北京市海淀区学院路38号
个人简介
北京大学临床医学高等研究院助理教授,博士生导师,生物医学工程研究中心独立PI,围绕化学与生命健康的交叉前沿开展化学生物学研究,重点发展具有高时空分辨能力的精准分子标记工具与成像技术,用于解析复杂生物体系中生物大分子的时空状态及其调控机制。
代表性工作包括:发展建立通用型超分辨膨胀显微成像技术,实现聚糖等多类生物大分子的纳米尺度空间分布解析(Nat. Methods 2021);构建化学–遗传编码分子记录器,结合组学分析与功能性基因筛选,解析复杂生物体系中蛋白激酶等信号通路的动态调控机制(Nat. Chem. Biol. 2025);开发可定向生物正交分子探针,实现疾病相关关键靶标的多模态高灵敏成像与分析(Angew. Chem. Int. Ed. 2022; Adv. Sci. 2026)。
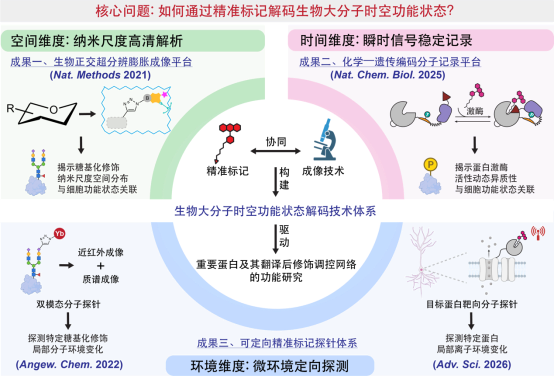
近年来,孙德恩博士担任多个国际期刊审稿人,并与北京大学、清华大学以及德国马克斯普朗克研究所等国内外高校和科研机构保持密切合作。课题组欢迎具有化学、生物、医学等背景的学生和博士后加入,鼓励开展交叉合作与国际交流。
科研与教育经历
2012.9 – 2016.6 武汉大学 化学学士
2016.9 – 2021.7 北京大学 化学生物学博士
2021.9 – 2026.3 德国马克斯普朗克医学研究所 博士后
2026.4 – 至今 北京大学临床医学高等研究院 助理教授/副研究员
主要研究方向
生物大分子的空间分布和动态活性共同塑造其时空状态,是维持细胞稳态和调控生理功能的重要基础;其异常与衰老及癌症等重大疾病密切相关。本课题组聚焦蛋白质及其翻译后修饰的动态调控,融合化学生物学、功能蛋白设计与光学成像,发展功能驱动的精准标记工具与成像技术,重点关注生物分子空间分布、动态信号传导及其功能输出之间的关系。
1. 发展新型分子记录技术用于细胞信号网络的时空解析
分子记录技术(Molecular recorder)通过将细胞经历的瞬时信号事件转化为稳定、可追溯的分子标记,从而支持后续成像、分选与组学等多模态分析。本课题组将结合生物正交化学与蛋白质工程,发展高灵敏度、高时空特异性的分子记录工具,用于活细胞及复杂生物体系中关键信号传导过程的稳定记录,并进一步整合组学分析与功能筛选,建立“信号动态–细胞状态–分子特征”之间的系统关联。
2. 发展精准标记驱动的膨胀显微成像技术用于病理与药理研究
膨胀显微成像技术(Expansion microscopy)通过物理扩展生物样品,在保持原位结构信息的同时实现纳米尺度空间分辨率,并兼具组织透明化等优势。本课题组将结合新型组织–凝胶化学与核酸编码策略,构建具备高分辨率、多靶标能力的三维组织成像平台,重点解析细胞界面聚糖在纳米尺度上的空间分布与功能关联,推动该技术在动物模型和临床样本中的高分辨病理与药理研究应用。
3. 神经–肿瘤互作的化学解码
中枢神经系统肿瘤常形成高度互联的功能网络,并通过信号转导和物理连接重塑神经微环境,从而促进肿瘤增殖、迁移与侵袭。本课题组将结合分子记录与高分辨成像技术,原位捕捉肿瘤网络中的关键信号事件,解析肿瘤、神经与免疫细胞在微环境中的三维空间结构与互作模式,并结合药物干预与功能评估,探索神经–肿瘤互作中的关键调控环节及其潜在干预可能。
代表性科研项目
1. 2022.11 – 2024.11 Engineering of chemogenetic integrators for imaging kinase activities. 德国洪堡基金会,65 万元,主持
2. 2023.01 – 2024.12 Spying on brain tumors with chemogenetic integrators. 德国巴登-符腾堡州政府,62 万元,主持
10篇代表性论文
1. Sun, D.*, Ng, S., Zheng, Y., Xie, S., Schwan, N., Breuer, P., Hoffmann, D., Michel, J., Azorin, D., Boonekamp, K., Winkler, F., Wick, W., Boutros, M., Li, Y., Johnsson, K.* Molecular recording of cellular kinase activity with chemical labeling. Nat. Chem. Biol. 2025, 21, 1818–1827.
2. Sun, D., Fan, X., Shi, Y., Zhang, H., Huang, Z., Cheng, B., Tang, Q., Li, W., Zhu, Y., Bai, J., Liu, W., Li, Y., Wang, X., Lei, X., Chen, X.* Click-ExM enables expansion microscopy for all biomolecules. Nat. Methods 2021, 18, 107–113.
3. Wang, M.#, Sun, D.#, Gries, K., Johnsson, K.* Localizable fluorescent metal ion indicators with tunable colors. Adv. Sci. 2026. (In press)
4. Jin, G.#, Sun, D.#, Xia, X., Jiang, Z., Cheng, B., Ning, Y., Wang, F., Zhao, Y.*, Chen, X.*, Zhang, J.* Bioorthogonal lanthanide molecular probes for near-infrared fluorescence and mass spectrometry imaging. Angew. Chem. Int. Ed. 2022, 61, e202208707. (Selected as the inside back cover and VIP paper)
5. Sun, D., Chen, X.* Raman imaging shines a light on neurodegenerative disorders. ACS Cent. Sci. 2020, 6, 459–460. (Commentary article)
6. Lin, Y, Kompa, J., Sun, D., Mao, R., Koch, B., Hinnah, K., Wilhelm, J., Franz, N., Kühn, S., Menche, T., Adow, A., Breuer, P., Hiblot, J.*, Johnsson, K.* A high-affinity split-HaloTag for live-cell protein labeling. Nat. Commun. 2026, 17, 2865.
7. Xia, X., Sun, D., Tang, Q., Liu, X., Fan, X., Wan, Y., Cui, S., Zhang, X., Liu, Q., Jiang, Y., Wu, Y., Chen, X.* Fast metabolic glycan labeling for click-labeling and imaging of sialoglycans in living acute brain slices from mice and human patients. J. Am. Chem. Soc. 2024, 146, 22008–22016.
8. Fan, X.#, Song, Q.#, Sun, D., Hao, Y., Wang, J., Wang, C., Chen, X.* Cell-type-specific labeling and profiling of glycans in living mice. Nat. Chem. Biol. 2022, 18, 625–633.
9. Zhao, W.#, Zhao, S.#, Li, L.#, Huang, X., Xing, X., Zhang, Y., Qiu, G., Han, Z., Shang, Y., Sun, D., Shan, C., Wu, R., Zhang, S., Chen, R., Xiao, J., Mo, Y., Wang, J., Ji, W., Chen, X., Ding, B., Liu, Y., Mao, H., Song, B., Tan, J., Liu, J., Li, H.*, Chen, L.* Sparse deconvolution improves the resolution of live-cell super-resolution fluorescence microscopy. Nat. Biotechnol. 2022, 40, 606–617.
10. Hao, Y.#, Fan, X.#, Shi, Y., Zhang, C., Sun, D., Qin, K., Qin, W., Zhou, W., Chen, X.* Next-generation unnatural monosaccharides reveal that ESRRB O-GlcNAcylation regulates pluripotency of mouse embryonic stem cells. Nat. Commun. 2019, 10, 4065.
